Ստոպ կոդոն
Ստոպ կոդոն ՝ մոլեկուլային կենսաբանության մեջ (մասնավորապես՝ սպիտակուցի կենսասինթեզում) ստոպ կոդոնի նուկլեոտիդային եռյակը ի-ՌՆԹ-ում (ինֆորմացիոն կամ տեղեկատվական) ազդարարում է սինթեզվող սպիտակուցի թարգմանության (տրանսլիացիայի) գործընթացի ավարտը[1]։ Ինֆորմացիոն ՌՆԹ-ի կոդոնների մեծ մասը համապատասխանում է աճող պոլիպեպտիդային շղթայում ամինաթթվի ավելացմանը, որոնք էլ, ի վերջո, ձևավորում են սպիտակուցի մոլոկուլը։ Ստոպ կոդոններն ազդարարում են վերծանման կամ տրանսլիացիայի գործընթացի ավարտը նպաստելով ռիբոսոմային ենթամիավորների տարանջատմանը՝ ազատելով ամինաթթվային շղթան։
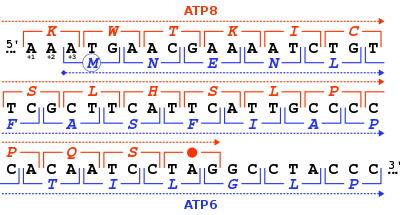
Հատկություններ
խմբագրելՍտանդարտ կոդոններ
խմբագրելՍտանդարտ գենետիկ կոդում կան երեք տարբեր ստոպ կոդոններ։
| Կոդոն | Ստանդարտ կոդ | անուն | ||
|---|---|---|---|---|
| Դնթ | ՌՆԹ | |||
TAG |
UAG
|
STOP = Ter (*)
|
սաթ | |
TAA |
UAA
|
STOP = Ter (*)
|
օխրա | |
TGA |
UGA
|
STOP = Ter (*)
|
օպալ կամ սաթ | |
Այլընտրանքային ստոպ կոդոններ
խմբագրելՍտանդարտ գենետիկ կոդի տատանումներ, և այլընտրանքային ստոպ կոդոններ հայտնաբերվել են նաև ողնաշարավորների միտոքոնդրիալ գենոմներում[2]։
| Գենետիկ կոդ | Translation table |
Codon | Translation with this code |
Standard translation | ||||
|---|---|---|---|---|---|---|---|---|
| DNA | RNA | |||||||
| Ողնաշարավորների միտոքոնդրիումում | 2 | AGA |
AGA |
STOP = Ter (*) |
Arg (R)
| |||
AGG |
AGG |
STOP = Ter (*) |
Arg (R)
| |||||
| բակտերիաներ | 22 | TCA |
UCA |
STOP = Ter (*) |
Ser (S)
| |||
| սնկեր | 23 | TTA |
UUA |
STOP = Ter (*) |
Leu (L)
| |||
| Ամինաթթուների կենսաքիմիական հատկությունները | Ոչ բևեռային | Բևեռային | Հիմնական | Թթվային | Դադարեցում՝ ստոպ կոդոն |
Վերանշանակված ստոպ կոդոններ
խմբագրելԿորիզային գենետիկ կոդը ճկուն է, ինչպես ցույց է տրված տարբեր գենետիկ կոդերով, որոնք ստանդարտ ստոպ կոդոնները վերագրում են ամինաթթուներին[3]։
Թարգմանություն
խմբագրել1986թ.-ին համոզիչ ապացույցներ ներկայացվեցին այն մասին, որ սելենոցիստեինը (Sec) կոդավորվում է մի քանի կոդոններով։ Ավելին, կոդոնը նույնականացվել է որպես UGA, որը նաև հայտնի է որպես օպալի ավարտման կոդոն (տերմինատոր կոդոն)[4]։ Էուկարիոտների և պրոկարիոտների մոտ նույնականացվել է այս կոդոնի իրականացրած գործառույթը[5]։ Այս թագավորությունների միջև առանձնահատուկ տարբերությունն այն է, որ cis տարրերը (Cis-կարգավորող տարրերը, ինչպիսիք են խթանողները, ուժեղացուցիչները և խլացուցիչները, ոչ կոդավորող ԴՆԹ-ի շրջաններ են, որոնք կարգավորում են մոտակա գեների տրանսկրիպցիան) սահմանափակված են UAG կոդոնի առկայությամբ պրոկարիոտներում, մինչդեռ էուկարիոտներում այս սահմանափակումը չկա[6]։
2003 թվականին իրականացվեց մարդկանց բոլոր հայտնի սելենոպրոտեինների նույնականացումը՝ ընդհանուր 25[7]։ Նմանատիպ անալիզներ են կատարվել այլ օրգանիզմների համար։
UAG կոդոնը կարող է թարգմանվել պիրոլիզինի (Pyl) նույն ձևով։
Գենոմային բաշխում
խմբագրելՍտոպ կոդոնների բաշխումը օրգանիզմի գենոմում պատահական չէ և կարող է փոխկապակցվել GC-ի պարունակության հետ[8][9]։ Օրինակ, E. coli K-12 գենոմը պարունակում է 2705 TAA (63%), 1257 TGA (29%) և 326 TAG (8%) ստոպ կոդոններ (GC պարունակությունը 50.8%)[10]։ GC- պարունակության լայն շրջանակ ունեցող բակտերիաների լայնածավալ ուսումնասիրությունը ցույց է տալիս, որ չնայած TAA-ի առաջացման հաճախականությունը բացասաբար է կապված GC-ի պարունակության հետ, իսկ TGA-ի առաջացման հաճախականությունը դրականորեն է կապված GC-ի պարունակության հետ։ TAG ստոպ կոդոնը, որը հաճախ նվազագույն օգտագործվող ստոպ կոդոնն է գենոմում, չի ազդում GC-ի պարունակության վրա[11]։
Ճանաչում
խմբագրելԲակտերիաներում ստոպ կոդոնների ճանաչումը կապված է այսպես կոչված «տրիպեպտիդ հակակոդոնի» հետ[12]։
Անվանակարգ
խմբագրելՍտոպ կոդոնները պատմականորեն ստացել են բազմաթիվ տարբեր անուններ, քանի որ յուրաքանչյուրը համապատասխանում էր մուտանտների առանձին դասի։ Այս մուտանտները սկզբում մեկուսացվել են բակտերիոֆագների (T4 և lambda) վիրուսների մեջ, որոնք վարակում են Escherichia coli բակտերիաները։ Վիրուսային գեների հատուկ մշակված մուտացիաները թուլացրել են նրանց վարակիչ կարողությունը՝ ստեղծելով այնպիսի վիրուսներ, որոնք կարողացել են վարակել և աճել միայն E. coli-ի որոշ տեսակների ներսում։
սաթի մուտացիաներ (UAG)
խմբագրելԴրանք հայտնաբերված անհեթեթ մուտացիաների առաջին խումբն էին, որոնք առանձնացրել են Ռիչարդ Հ. Էփշտեյնը և Չարլզ Սթայնբերգը և անվանվել ի պատիվ նրանց ընկերոջ և Կալտեխ շրջանավարտ Հարիս Բերնշտայնի, ում ազգանունը գերմաներեն նշանակում է «սաթ» (տես՝ Բերնշտեյն)[13][14]։
Սաթի մուտացիաներով վիրուսները օժտված են բակտերիաների միայն որոշակի շտամներ վարակելու ունակությամբ, որոնք հայտնի են որպես սաթի ճնշողներ։ Այս բակտերիաները կրում են իրենց սեփական մուտացիան, որը թույլ է տալիս վերականգնել մուտանտ վիրուսների գործառույթը։ Օրինակ, տ-ՌՆԹ-ի մուտացիան, որը ճանաչում է սաթի կանգառի կոդոնը, թարգմանությանը թույլ է տալիս «կարդալ» կոդոնը և արտադրել ամբողջ երկարությամբ սպիտակուց՝ դրանով իսկ վերականգնելով սպիտակուցի նորմալ ձևը և «ճնշել» սաթի մուտացիան[15]։ Այսպիսով, սաթի մուտանտները վիրուսային մուտանտների մի ամբողջ դաս են, որոնք կարող են աճել բակտերիաներում, որոնք պարունակում են սաթի ճնշող մուտացիաներ։ Նմանատիպ ճնշիչները հայտնի են նաև օխերայի և օպալի ստոպ կոդոնների համար։
տ-ՌՆԹ-ի մոլեկուլները, որոնք կրում են անբնական,ոչ ճիշտ ամինաթթուներ, նախագծվել են բակտերիալ ՌՆԹ-ում սաթի ստոպ կոդոնը ճանաչելու համար։ Այս տեխնոլոգիան թույլ է տալիս ներառել ամինաթթուներ (օրինակ՝ p-azidophenylalanine) թիրախային սպիտակուցի հատուկ վայրերում։
օխրա մուտացիաներ (UAA)
խմբագրելՀայտնաբերված երկրորդ ստոպ-կոդոնի մուտացիան էր։ Սաթի հետ կապված սովորական դեղին-նարնջագույն-շագանակագույն գույնը հիշեցնող այս երկրորդ ստոպ կոդոնը ստացել է «օխրա» անունը՝ նարնջագույն-կարմրավուն-շագանակագույն հանքային պիգմենտ[14]։
Մի շարք մուտացիոն փորձերի միջոցով, որոնք համեմատում էին այս մուտանտները միմյանց և այլ հայտնի ամինաթթուների կոդոնների հետ, Սիդնեյ Բրենները եզրակացրեց, որ սաթի և օխրայի մուտացիաները համապատասխանում են «UAG» և «UAA» նուկլեոտիդային եռյակներին[16]։
Մուտացիաներ և հիվանդություններ
խմբագրելՆոնսենս
խմբագրելՆոնսոնս մուտացիաները ԴՆԹ-ի հաջորդականության փոփոխություններն են, որոնք ներդնում են վաղաժամ կանգառի կոդոն, ինչի հետևանքով ստացված ցանկացած սպիտակուցի աննորմալ կրճատում։ Սա հաճախ հանգեցնում է սպիտակուցի ֆունկցիայի կորստի, քանի որ ամինաթթուների շղթայի կարևոր մասերն այլևս չեն հավաքվում։ Այս տերմինաբանության պատճառով ստոպ կոդոնները նաև անվանվել են անհեթեթ կոդոններ՝ նոնսենս։
Նոնստոպ՝անդադար մուտացիան, որը նաև կոչվում է «stop-loss» տարբերակ, կետային մուտացիա է, որը տեղի է ունենում ստոպ կոդոնի ներսում։ Նոնստոպ մուտացիաները հանգեցնում են ի- ՌՆԹ-ի շղթայի շարունակական թարգմանությանը, որը պետք է լինի չթարգմանված շրջան։ Շատ պոլիպեպտիդներ, որոնք առաջանում են Նոնստոպ մուտացիա ունեցող գենից, կորցնում են իրենց գործառույթը ծայրահեղ երկարության պատճառով։ Nonstop մուտացիաները տարբերվում են Նոնսենս մուտացիաներից նրանով, որ նրանք չեն ստեղծում ստոպ կոդոն, այլ, փոխարենը, ջնջում են մեկը:Նոնստոպ մուտացիաները նույնպես տարբերվում են անիմաստ մուտացիաներից, որոնք կետային մուտացիաներ են, որտեղ մեկ նուկլեոտիդը փոխվում է՝ փոխարինելու այլ ամինաթթուով։ Անդադար մուտացիաները կապված են բազմաթիվ ժառանգական հիվանդությունների հետ, ներառյալ էնդոկրին խանգարումները[17], աչքի հիվանդություն[18], և նյարդային զարգացման խանգարումներ[19][20]։
Թաքնված կանգառներ
խմբագրելԹաքնված կանգառները չդադարող կոդոններ են, որոնք կարող են կարդացվել որպես կանգառ կոդոններ։ Դրանք վաղաժամկետ դադարեցնում են թարգմանությունը, եթե համապատասխան շրջանակի տեղաշարժը (օրինակ՝ ռիբոսոմային ՌՆԹ-ի սայթաքման պատճառով) տեղի է ունենում մինչև թաքնված կանգառը։ Ենթադրվում է, որ դա նվազեցնում է ռեսուրսների վատնումը ոչ ֆունկցիոնալ սպիտակուցների վրա և պոտենցիալ ցիտոտոքսինների արտադրությունը։ Լուիզիանայի պետական համալսարանի հետազոտողները առաջարկում են մեկ այլ վարկած, որի համար ընտրվում են թաքնված կանգառներ։ Կոդոնները, որոնք կարող են ձևավորել թաքնված կանգառներ, ավելի հաճախ օգտագործվում են գենոմներում, որոնք այլ կերպ կոդավորում են նույն ամինաթթուն։ Օրգանիզմում անկայուն ռ-ՌՆԹ փոխկապակցված է թաքնված կանգառների հետ[21]։ Այնուամենայնիվ, այս վարկածը չի կարող հաստատվել[22]։
Ստոպ-կոդոնները և թաքնված կանգառները միասին կոչվում են կանգառ ազդանշաններ։ Մեմֆիսի համալսարանի գիտնականները պարզել են, որ գենետիկորեն առնչվող բակտերիաների գրեթե նույնական գենոմային-TSSR ( թարգմանության ստոպ ազդանշանների հարաբերակցություն կամ TSSR)արժեքը կարող է հուշել, որ բակտերիալ գենոմի ընդլայնումը սահմանափակված է այդ բակտերիաների տեսակների իրենց եզակի ստոպ ազդանշաններով:.[23]
Թարգմանական ընթերցում
խմբագրելՍտոպ կոդոնի ճնշումը կամ թարգմանական ընթերցումը տեղի է ունենում, երբ թարգմանության մեջ կանգառ կոդոնը մեկնաբանվում է որպես իմաստային կոդոն, այսինքն՝ երբ (ստանդարտ) ամինաթթուն «կոդավորվում» է ստոպ կոդոնով։ Թարգմանական ընթերցումը շատ տարածված է վիրուսների և բակտերիաների մեջ, ինչպես նաև հայտնաբերվել է որպես գեների կարգավորման սկզբունք մարդկանց, խմորիչների, բակտերիաների և դրոզոֆիլայի մոտ[24][25]։ Մարդու մալատդեհիդրոգենազի դեպքում ստոպ կոդոնը ընթերցվում է մոտ 4% հաճախականությամբ[26]։
Օգտագործում որպես ջրանիշ
խմբագրել2010 թվականին, երբ Քրեյգ Վենթերը ներկայացրեց առաջին լիարժեք գործող, սինթետիկ ԴՆԹ-ով վերահսկվող վերարտադրող բջիջը, նա նկարագրեց, թե ինչպես է իր թիմն օգտագործում հաճախակի ստոպ կոդոններ ՌՆԹ-ում և ԴՆԹ-ում ջրանիշներ ստեղծելու համար[27]։
Ծանոթագրություններ
խմբագրել- ↑ Griffiths AJF, Miller JH, Suzuki DT, Lewontin RC, Gelbart WM (2000). «Chapter 10 (Molecular Biology of Gene Function): Genetic code: Stop codons». An Introduction to Genetic Analysis. W.H. Freeman and Company.
- ↑ Wideman, Jeremy G.; Monier, Adam; Rodríguez-Martínez, Raquel; Leonard, Guy; Cook, Emily; Poirier, Camille; Maguire, Finlay; Milner, David S.; Irwin, Nicholas A. T.; Moore, Karen; Santoro, Alyson E. (2019 թ․ նոյեմբերի 25). «Unexpected mitochondrial genome diversity revealed by targeted single-cell genomics of heterotrophic flagellated protists». Nature Microbiology (անգլերեն). 5 (1): 154–165. doi:10.1038/s41564-019-0605-4. hdl:10871/39819. ISSN 2058-5276. PMID 31768028. S2CID 208279678.
- ↑ Swart, Estienne Carl; Serra, Valentina; Petroni, Giulio; Nowacki, Mariusz (2016). «Genetic Codes with No Dedicated Stop Codon: Context-Dependent Translation Termination». Cell. 166 (3): 691–702. doi:10.1016/j.cell.2016.06.020. PMC 4967479. PMID 27426948.
- ↑ Zinoni, F; Birkmann, A; Stadtman, T; Böck, A (1986). «Nucleotide sequence and expression of the selenocysteine-containing polypeptide of formate dehydrogenase (formate-hydrogen-lyase-linked) from Escherichia coli». Proceedings of the National Academy of Sciences. 83 (13): 4650–4654. Bibcode:1986PNAS...83.4650Z. doi:10.1073/pnas.83.13.4650. PMC 323799. PMID 2941757.
- ↑ Böck, A (2013). «Selenoprotein Synthesis». Encyclopedia of Biological Chemistry. էջեր 210–213. doi:10.1016/B978-0-12-378630-2.00025-6. ISBN 9780123786319. Վերցված է 2021 թ․ օգոստոսի 23-ին.
- ↑ Mix, H; Lobanov, A; Gladyshev, V (2007). «SECIS elements in the coding regions of selenoprotein transcripts are functional in higher eukaryotes». Nucleic Acids Research. 35 (2): 414–423. doi:10.1093/nar/gkl1060. PMC 1802603. PMID 17169995.
- ↑ Kryukov, G; Gladyshev, V (2003). «Characterization of mammalian selenoproteomes». Science. 300 (5624): 1439–1443. Bibcode:2003Sci...300.1439K. doi:10.1126/science.1083516. PMID 12775843. S2CID 10363908.
- ↑ Povolotskaya IS, Kondrashov FA, Ledda A, Vlasov PK (2012). «Stop codons in bacteria are not selectively equivalent». Biology Direct. 7: 30. doi:10.1186/1745-6150-7-30. PMC 3549826. PMID 22974057.
{{cite journal}}: CS1 սպաս․ չպիտակված ազատ DOI (link) - ↑ Korkmaz, Gürkan; Holm, Mikael; Wiens, Tobias; Sanyal, Suparna (2014). «Comprehensive Analysis of Stop Codon Usage in Bacteria and Its Correlation with Release Factor Abundance». The Journal of Biological Chemistry. 289 (44): 775–806. doi:10.1074/jbc.M114.606632. PMC 4215218. PMID 25217634.
- ↑ «Escherichia coli str. K-12 substr. MG1655, complete genome [Genbank Accession Number: U00096]». GenBank. NCBI. Վերցված է 2013 թ․ հունվարի 27-ին.
- ↑ Wong, Tit-Yee; Fernandes, Sanjit; Sankhon, Naby; Leong, Patrick P; Kuo, Jimmy; Liu, Jong-Kang (2008). «Role of Premature Stop Codons in Bacterial Evolution». Journal of Bacteriology. 190 (20): 6718–6725. doi:10.1128/JB.00682-08. PMC 2566208. PMID 18708500.
- ↑ Ito, Koichi; Uno, Makiko; Nakamura, Yoshikazu (1999). «A tripeptide 'anticodon' deciphers stop codons in messenger RNA». Nature. 403 (6770): 680–684. doi:10.1038/35001115. PMID 10688208. S2CID 4331695.
- ↑ Stahl FW (1995). «The amber mutants of phage T4». Genetics. 141 (2): 439–442. doi:10.1093/genetics/141.2.439. PMC 1206745. PMID 8647382.
- ↑ 14,0 14,1 Lewin, Benjamin; Krebs, Jocelyn E.; Goldstein, Elliott S.; Kilpatrick, Stephen T. (2011 թ․ ապրիլի 18). Lewin's Essential GENES (անգլերեն). Jones & Bartlett Publishers. ISBN 978-1-4496-4380-5.
- ↑ Robin Cook. «Amber, Ocher, and Opal Mutations Summary». World of Genetics. Gale.
- ↑ Brenner, S.; Stretton, A. O. W.; Kaplan, S. (1965). «Genetic Code: The 'Nonsense' Triplets for Chain Termination and their Suppression». Nature. 206 (4988): 994–8. Bibcode:1965Natur.206..994B. doi:10.1038/206994a0. PMID 5320272. S2CID 28502898.
- ↑ Pang S.; Wang W.; և այլք: (2002). «A novel nonstop mutation in the stop codon and a novel missense mutation in the type II 3beta-hydroxysteroid dehydrogenase (3beta-HSD) gene causing, respectively, nonclassic and classic 3beta-HSD deficiency congenital adrenal hyperplasia». J Clin Endocrinol Metab. 87 (6): 2556–63. doi:10.1210/jcem.87.6.8559. PMID 12050213.
- ↑ Doucette, L.; և այլք: (2011). «A novel, non-stop mutation in FOXE3 causes an autosomal dominant form of variable anterior segment dysgenesis including Peters anomaly». European Journal of Human Genetics. 19 (3): 293–299. doi:10.1038/ejhg.2010.210. PMC 3062009. PMID 21150893.
- ↑ Torres-Torronteras, J.; Rodriguez-Palmero, A.; և այլք: (2011). «A novel nonstop mutation in TYMP does not induce nonstop mRNA decay in a MNGIE patient with severe neuropathy» (PDF). Hum. Mutat. 32 (4): E2061–E2068. doi:10.1002/humu.21447. PMID 21412940. S2CID 24446773.
- ↑ Spaull, R; Steel, D; Barwick, K; Prabhakar, P; Wakeling, E; Kurian, MA (2022 թ․ հուլիսի 23). «STXBP1 Stop‐Loss Mutation Associated with Complex Early Onset Movement Disorder without Epilepsy». Movement Disorders Clinical Practice (անգլերեն). 9 (6): 837–840. doi:10.1002/mdc3.13509. ISSN 2330-1619. PMC 9346254. PMID 35937496.
- ↑ Seligmann, Hervé; Pollock, David D. (2004). «The Ambush Hypothesis: Hidden Stop Codons Prevent Off-Frame Gene Reading». DNA and Cell Biology. 23 (10): 701–5. doi:10.1089/1044549042476910. PMID 15585128.
- ↑ Cavalcanti, Andre; Chang, Charlotte H.; Morgens, David W. (2013). «Ambushing the ambush hypothesis: predicting and evaluating off-frame codon frequencies in Prokaryotic Genomes». BMC Genomics. 14 (418): 1–8. doi:10.1186/1471-2164-14-418. PMC 3700767. PMID 23799949.
{{cite journal}}: CS1 սպաս․ չպիտակված ազատ DOI (link) - ↑ Wong, Tit-Yee; Schwartzbach, Steve (2015). «Protein mis-termination initiates genetic diseases, cancers, and restricts bacterial genome expansion». Journal of Environmental Science and Health, Part C. 33 (3): 255–85. doi:10.1080/10590501.2015.1053461. PMID 26087060. S2CID 20380447.
- ↑ Namy O, Rousset JP, Napthine S, Brierley I (2004). «Reprogrammed genetic decoding in cellular gene expression». Molecular Cell. 13 (2): 157–68. doi:10.1016/S1097-2765(04)00031-0. PMID 14759362.
- ↑ Schueren F, Lingner T, George R, Hofhuis J, Gartner J, Thoms S (2014). «Peroxisomal lactate dehydrogenase is generated by translational readthrough in mammals». eLife. 3: e03640. doi:10.7554/eLife.03640. PMC 4359377. PMID 25247702.
{{cite journal}}: CS1 սպաս․ չպիտակված ազատ DOI (link) - ↑ Hofhuis J, Schueren F, Nötzel C, Lingner T, Gärtner J, Jahn O, Thoms S (2016). «The functional readthrough extension of malate dehydrogenase reveals a modification of the genetic code». Open Biol. 6 (11): 160246. doi:10.1098/rsob.160246. PMC 5133446. PMID 27881739.
- ↑ «Watch me unveil "synthetic life"». 2010 թ․ մայիսի 21.
| Վիքիպահեստն ունի նյութեր, որոնք վերաբերում են «Ստոպ կոդոն» հոդվածին։ |